Bactéria degrada atrazina e nicosulfuron no solo
Cepa YB01 reduz resíduos de herbicidas e melhora atributos químicos e biológicos do solo
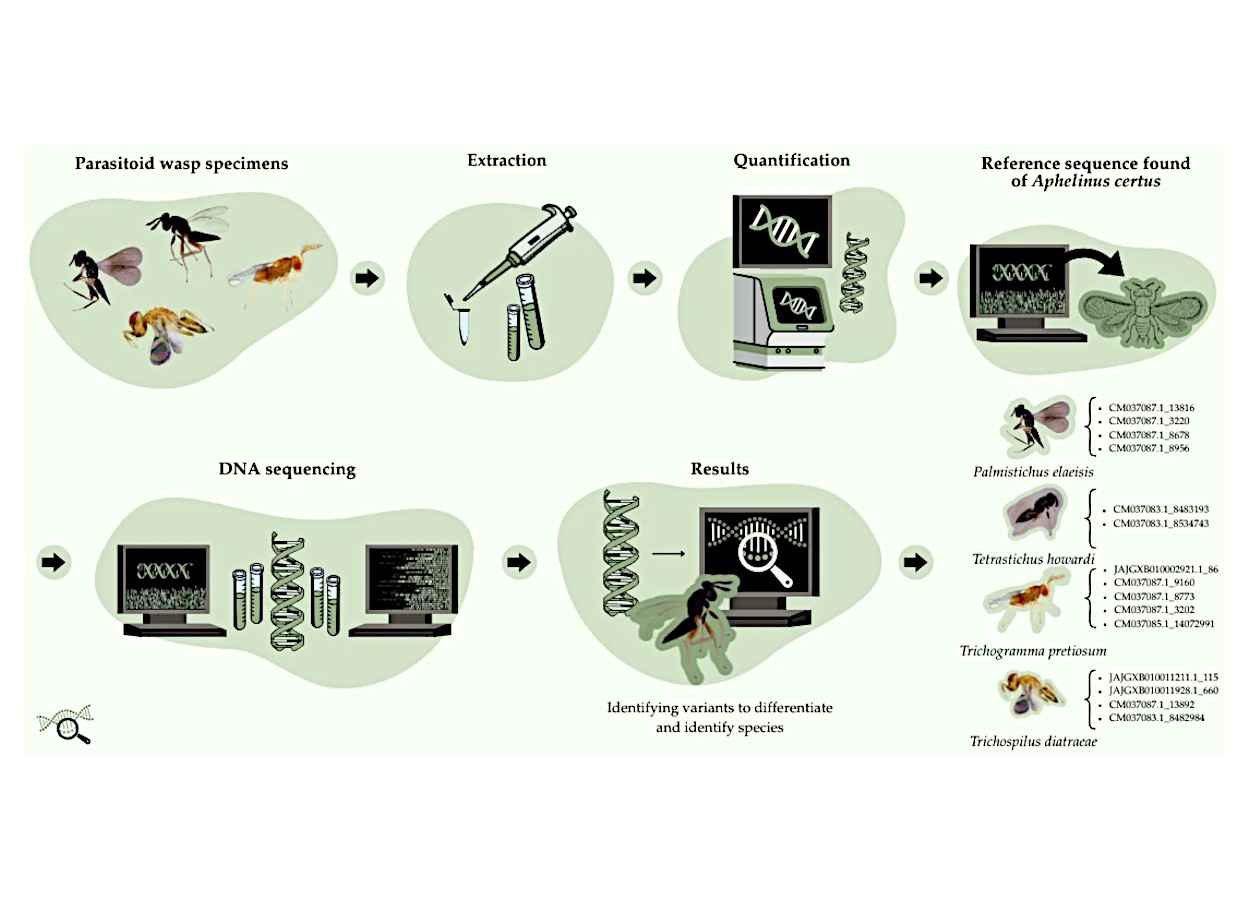
A identificação molecular de parasitoides por sequenciamento genômico completo elevou a precisão na distinção de espécies utilizadas no controle biológico. Estudo conduzido por pesquisadores brasileiros identificou variantes genéticas específicas para quatro agentes amplamente usados em programas agrícolas: Palmistichus elaeisis, Tetrastichus howardi, Trichospilus diatraeae e Trichogramma pretiosum.
O trabalho utilizou sequenciamento completo do genoma com a plataforma Illumina NovaSeq 6000. A abordagem permitiu detectar variantes específicas em cada espécie. Foram identificadas quatro variantes para Palmistichus elaeisis, duas para Tetrastichus howardi, quatro para Trichospilus diatraeae e cinco para Trichogramma pretiosum. Esses marcadores possibilitam discriminação individual precisa entre espécies morfologicamente semelhantes.
A identificação tradicional baseada em morfologia apresenta limitações. Os parasitoides analisados possuem tamanho reduzido e alta similaridade estrutural. Isso dificulta diagnósticos em campo e exige conhecimento taxonômico especializado. O estudo demonstra que variantes genômicas superam essas limitações ao fornecer diferenciação baseada em DNA.
Os insetos avaliados atuam no controle de lepidópteros de importância econômica. Entre os alvos, destacam-se pragas como Diatraea saccharalis e Thyrinteina arnobia. Essas espécies causam danos em culturas como cana-de-açúcar e eucalipto. A correta identificação dos parasitoides impacta diretamente a eficiência das liberações em campo.
A análise utilizou ferramentas bioinformáticas para controle de qualidade, alinhamento e detecção de variantes. O genoma de referência Aphelinus certus apresentou melhor desempenho. Esse material mostrou maior consistência na identificação de variantes e melhor alinhamento entre espécies analisadas.
A análise de componentes principais separou claramente as espécies com base nos dados genéticos. O componente principal PC1 explicou 51,12% da variação total e isolou Trichogramma pretiosum das demais. Já a análise de distância euclidiana confirmou maior proximidade genética entre Trichospilus diatraeae e Tetrastichus howardi.
O estudo também testou a robustez dos marcadores em amostras simuladas. Os resultados indicaram alta precisão mesmo em misturas com proporções desbalanceadas entre espécies. Essa capacidade amplia o uso da ferramenta em situações de campo e em biofábricas.
A aplicação prática inclui controle de qualidade em produção massal de parasitoides. Programas comerciais multiplicam esses insetos por várias gerações. Esse processo pode reduzir variabilidade genética. O uso de marcadores genômicos permite monitoramento contínuo das populações.
O trabalho foi desenvolvido por Izabella de Lima Palombo, Fabricio Fagundes Pereira, André Pessoa da Costa, Patrik Luiz Pastori, Alex Polatto Carvalho, Andrea Renata da Silva Romero, André Vieira do Nascimento, Ana Maria Perez Obrien, Patricia Iana Schmidt, Carlos Reinier Garcia Cardoso e Marcelo Teixeira Tavares.
Mais informações em doi.org/10.3390/insects17040395

Receba por e-mail as últimas notícias sobre agricultura